吉林大学生命科学学院韩葳葳教授、美国密苏里大学电气工程和计算机科学系许东教授科研团队提出一种高效、可操作性强的分子动力学模拟分析方法(NRI-MD),该方法首次将深度学习的图神经网络(GNN)运用于分子动力学模拟分析,基于模拟轨迹的原子速度和位置数据,通过神经关系推理模型(NRI)直接推断出酶分子动力学模拟中残基的相互作用模式,推断出酶的别构调控路径以及氨基酸突变后相对自由能的变化。NRI-MD模型的提出为蛋白质(酶)结构-功能研究领域提供了一种新构架,有望开辟酶分子设计的新模式。研究成果于2022年03月29日在学术期刊《Nature Communications》正式发表(Neural relational inference to learn long-range allosteric interactions in proteins from molecular dynamics simulations)。论文第一完成单位为吉林大学生命科学学院,吉林大学生命科学学院朱镜璇博士和密苏里大学计算机科学系王珏鑫博士为该论文的共同第一作者,吉林大学韩葳葳教授和密苏里大学许东教授为该论文的共同通讯作者。

分子动力学(MD)模拟已经成为一种成熟的技术手段来探究生物学过程中涉及的各种动态调控过程,深刻地促进了生命科学和药物研发等领域的长足发展,2013年马丁·卡普拉斯等三位科学家因此荣获诺贝尔奖。然而,由于模拟时间尺度的局限性以及模拟轨迹数据的高维度性和复杂性,难以从轨迹中获得与远程调控或构象变化直接相关的氨基酸非线性关系。许东教授、韩葳葳教授团队通过深入合作,将最前沿的深度学习的方法NRI运用于生物大分子动力学模拟轨迹的分析中,根据已有的模拟轨迹数据,NRI-MD可以显示出隐藏的离散图结构,以图结构作为引导输出重构轨迹,全程以无监督的方式最小化重构轨迹和输入轨迹之间的重构误差,抽象了在构象转变中潜在的关系结构,有潜力展示出与功能直接相关的交互关系模式(图1)。该研究应用NRI-MD对Pin1、SOD1和MEK1三种酶的别构调控过程进行了深入研究,成功地捕获了驱动酶分子复杂运动的氨基酸相互作用模式以及远端残基扰动介导活性位点残基构象重排的别构调控路径(图2)。
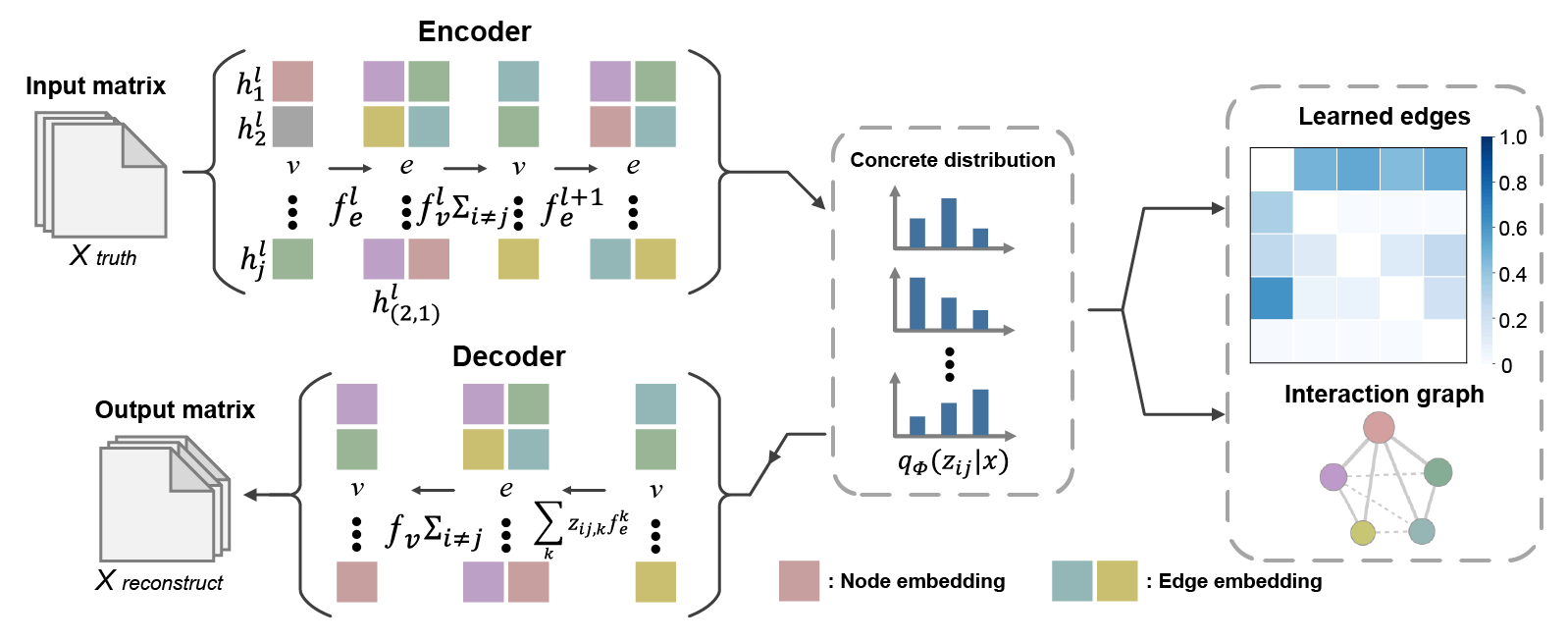
图1:NRI深度学习框架
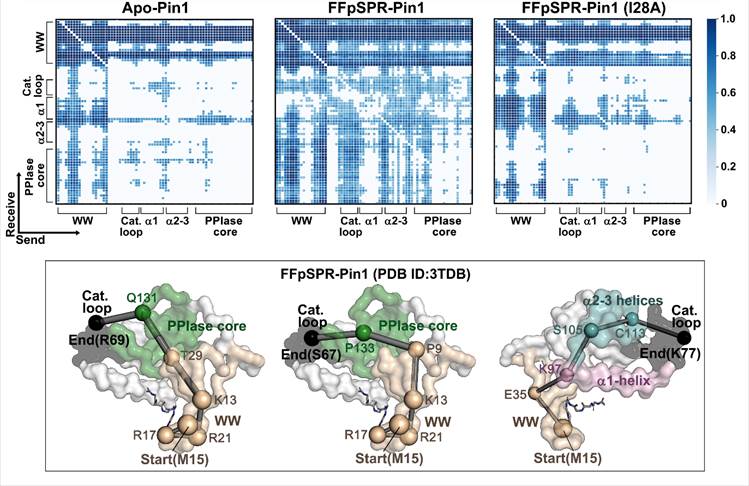
图2: Pin1 别构调控路径研究
此外,为评估 NRI-MD的有效性和鲁棒性,该研究对 NRI-MD和其它分析方法(Hessian 矩阵分析、CNA 分析)进行比较。NRI-MD的轨迹分析方法有以下优点:(1)捕捉信号时效性更优,该模型能够在结构构象完全变化前(模拟早期)捕捉到传递至催化环(Cat. loop)的信号(图3a);(2)准确性更好,在预测氨基酸突变引发的相对自由能变方面,该模型计算的 ddG 值与实验值的相关性更高(图 3b)。此研究表明,NRI-MD相比于传统MD的分析方法,在时效性和信噪比方面具有显著的提升,对酶分子的设计、再改造以及对相关疾病的理解提供了全新思路。从长远来看,本研究对加深图机器学习在分子动力学模拟领域的应用具有重要意义,同时为获取隐藏在生物大分子功能下的高层次特征提供了一种高效的技术方法。
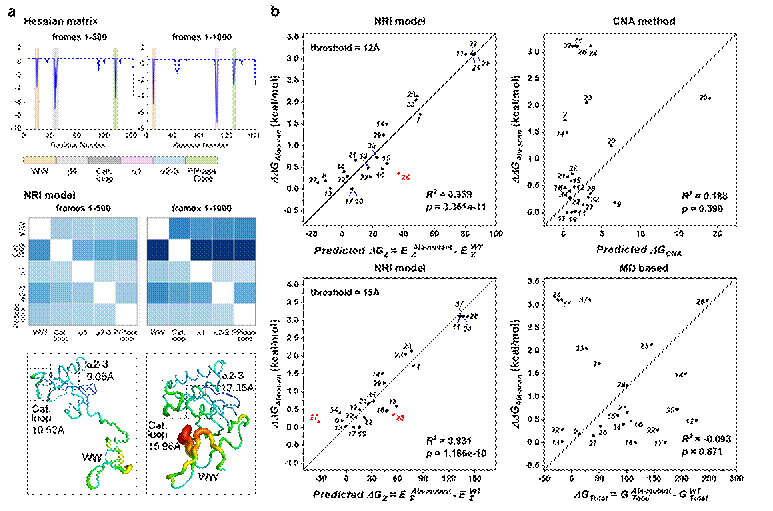
图3:NRI模型和其他分析方法的比较
该研究工作得到了吉林省海外合作项目(20200801069GH)的资助。同时对国家留学基金委、美国国立卫生研究院普通医学研究所以及密苏里大学Lewis HPC集群的支持表示由衷的感谢!
全文链接:https://www.nature.com/articles/s41467-022-29331-3